

在肝病诊疗领域,如何早期识别乙肝相关肝衰竭患者的继发感染风险一直是临床痛点。由于继发感染在早期往往缺乏典型的临床症状,致使约三分之一的感染病例直至患者入院后才被察觉,大幅增加患者死亡风险。
2026年3月3日,首都医科大学附属北京地坛医院金荣华院长,侯艺鑫主任,孙亚民研究员团队在Nature Communications杂志上发表题为“Proteomics-based machine learning model for predicting secondary infection in HBV-related liver failure”文章。本研究通过蛋白质组学与机器学习相结合的方法,开发出可早期预测继发感染的创新模型。首次系统描绘了乙肝相关肝衰竭继发感染的蛋白质组学图谱,为临床早期干预提供了全新的解决方案。拜谱生物为该研究提供了超高深度血液蛋白质组和PRM靶向蛋白质组技术服务。

英文标题:Proteomics-based machine learning model for predicting secondary infection in HBV-related liver failure
中文标题:基于蛋白质组学的机器学习模型用于预测HBV相关肝衰竭的继发感染
客户单位:首都医科大学附属北京地坛医院
研究材料:血浆
拜谱提供技术:超高深度血液蛋白质组和PRM靶向蛋白质组、机器学习分析
技术路线:
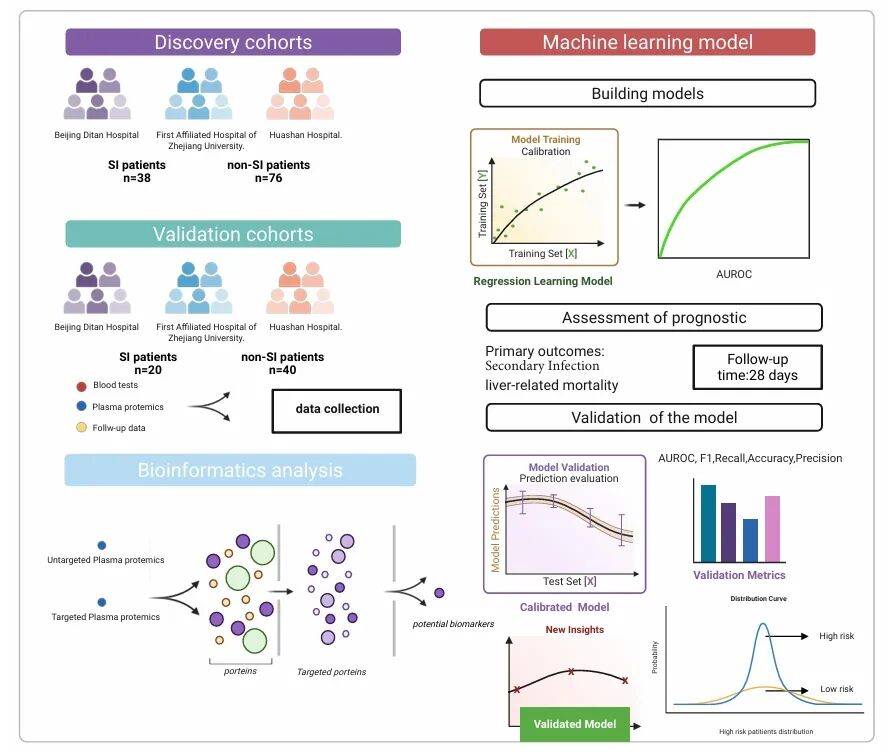
研究结果
1、从临床痛点出发:明确继发感染(SI)预测的未满足需求
为了突破传统预测模型的局限性,研究团队首先系统分析了乙型肝炎病毒(HBV)相关肝衰竭患者继发感染的临床特征。通过前瞻性多中心研究设计,在发现队列纳入114例患者,两个验证队列各纳入60例患者,发现SI患者普遍存在更严重的肝功能损伤、高黄疸水平以及凝血功能障碍。值得注意的是,入院时常规炎症标志物(如CRP、WBC)在SI与非SI患者间无显著差异,凸显了传统指标在早期预测中的局限性,也印证了开发新型分子预测模型的必要性。
2、血液蛋白质组学发现:揭示SI的分子特征
为探索继发感染的分子机制,研究团队对发现队列进行DB纳米磁珠富集(DBE kit)的非靶向血液蛋白质组学分析,共鉴定出974个差异表达蛋白(DEPs),其中炎症相关蛋白占27%,凝血相关蛋白占19%(图1a-c)。KEGG通路富集分析,显示血小板激活、补体凝血级联等通路显著失调。
进一步的相关性分析揭示了炎症与凝血系统的密切交互:炎症蛋白CALCA、SAA2与CRP呈强正相关,而凝血相关蛋白PLAT与CRP呈显著负相关;凝血指标PT、INR则与炎症调节因子TNFAIP6、IL1RL1等显著相关(图1d-g)。这些发现首次从分子层面证实了炎症-凝血轴在SI发病中的核心作用。
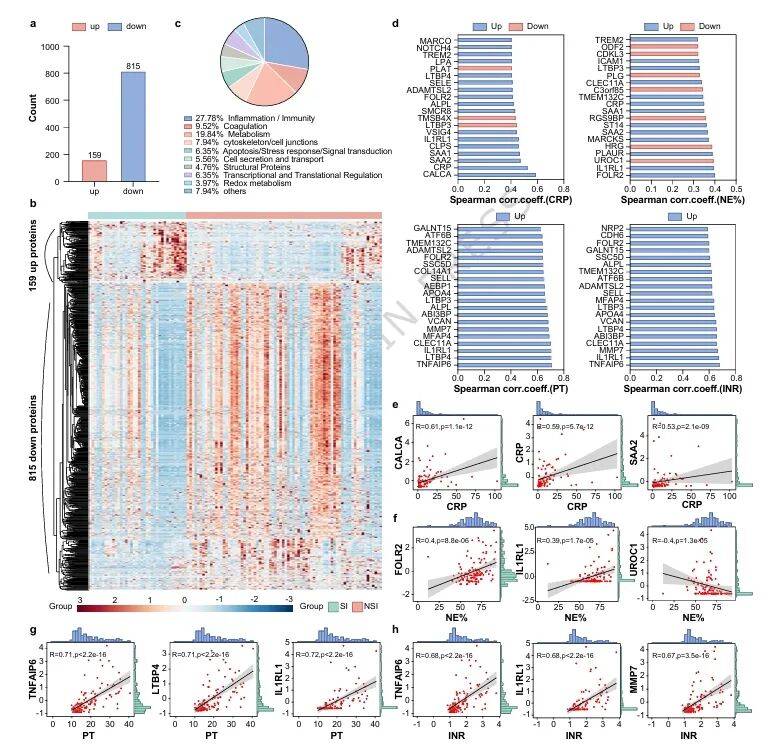 图1 非靶向血液蛋白质组学在发现队列中的结果编辑
图1 非靶向血液蛋白质组学在发现队列中的结果编辑
3、靶向蛋白质组学:验证关键标志物
基于非靶向的发现,研究团队在验证队列中采用PRM靶向蛋白质组学技术对31个候选蛋白进行验证。结果显示,继发感染组中炎症/免疫相关蛋白占24%,凝血相关蛋白占27%,进一步证实了炎症-凝血失衡的核心作用(图2a-c)。
相关性分析发现,凝血因子F2、ITGA2B、Serpin C1等与CRP、NE%显著相关,而急性期反应蛋白SAA1、S100A9、LYZ等与PT、INR呈强正相关(图2d)。这些靶向验证结果为模型构建提供了可靠的分子标志物。
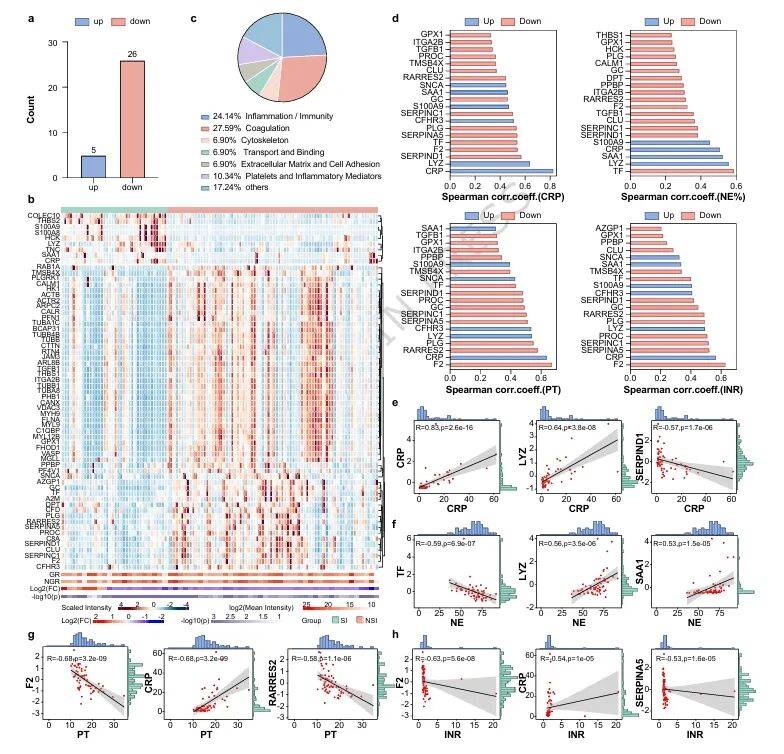 图2 靶向蛋白质组学在验证队列中的结果编辑
图2 靶向蛋白质组学在验证队列中的结果编辑
4、机器学习建模:构建预测性能卓越的模型
为实现精准风险预测,研究团队比较了五种机器学习算法,最终选择逻辑回归(LR)作为核心分类器,基于mRMR算法筛选的10个核心蛋白标志物(CALM1、LYZ、TMSB4X、GC、CRP、Serpin D1、DPT、A2M、PF4V1和SNCA)(图3d-f),结合AST和Tbil水平,研究团队构建了逻辑回归预测模型(Model 1)。进一步筛选出6个独立预测因子:4个蛋白标志物(LYZ、CALM1、Serpin D1、DPT)和2个临床指标(AST、Tbil)作为预测模型(Model 2)。
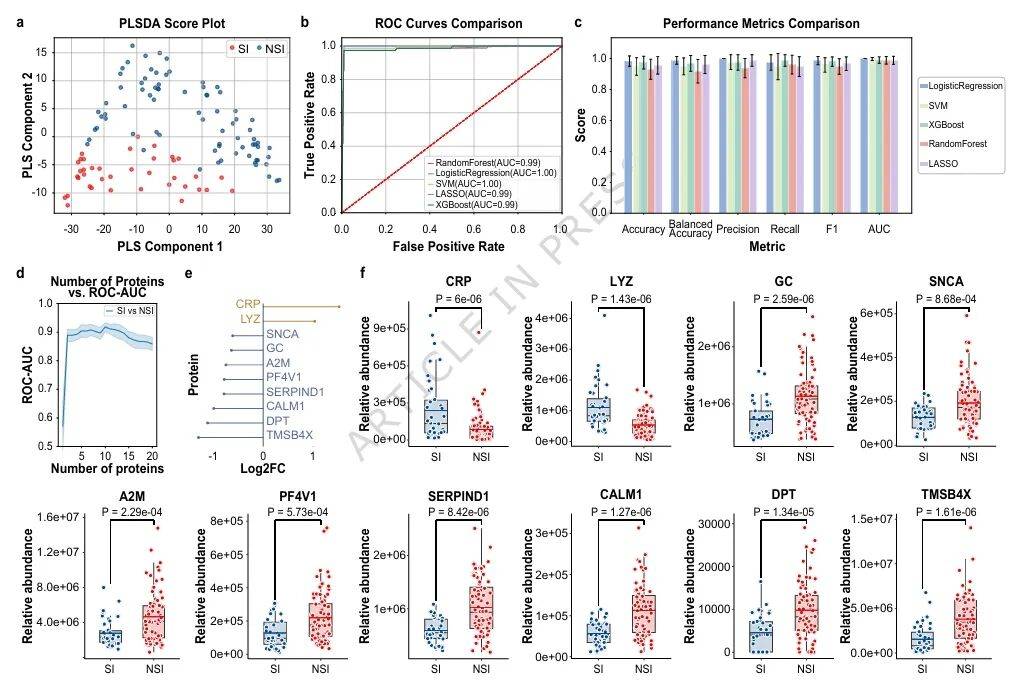 图3 模型1在发现队列中的表现编辑
图3 模型1在发现队列中的表现编辑
在发现队列中,Model 1的AUROC达0.980,优于Model 2(0.973)、传统炎症指标CRP(0.645)、WBC(0.674)和NE%(0.642)。在28天死亡率预测方面,Model 1 AUROC达0.883,优于CLIF-C ACLF评分(0.545)。(图4)
 图4 多种模型在发现队列中的表现编辑
图4 多种模型在发现队列中的表现编辑
5、多维度验证:确证模型的稳健性与临床适用性
在验证队列中,Model 1持续保持高预测准确性(AUROC=0.873),且显著优于其他指标(图5)。通过ELISA技术对核心蛋白标志物进行定量验证,发现LYZ在SI患者中显著升高,而CALM1、Serpin D1和DPT水平降低。基于ELISA数据的模型同样达到0.883的AUROC值,证实了其临床应用的可行性。
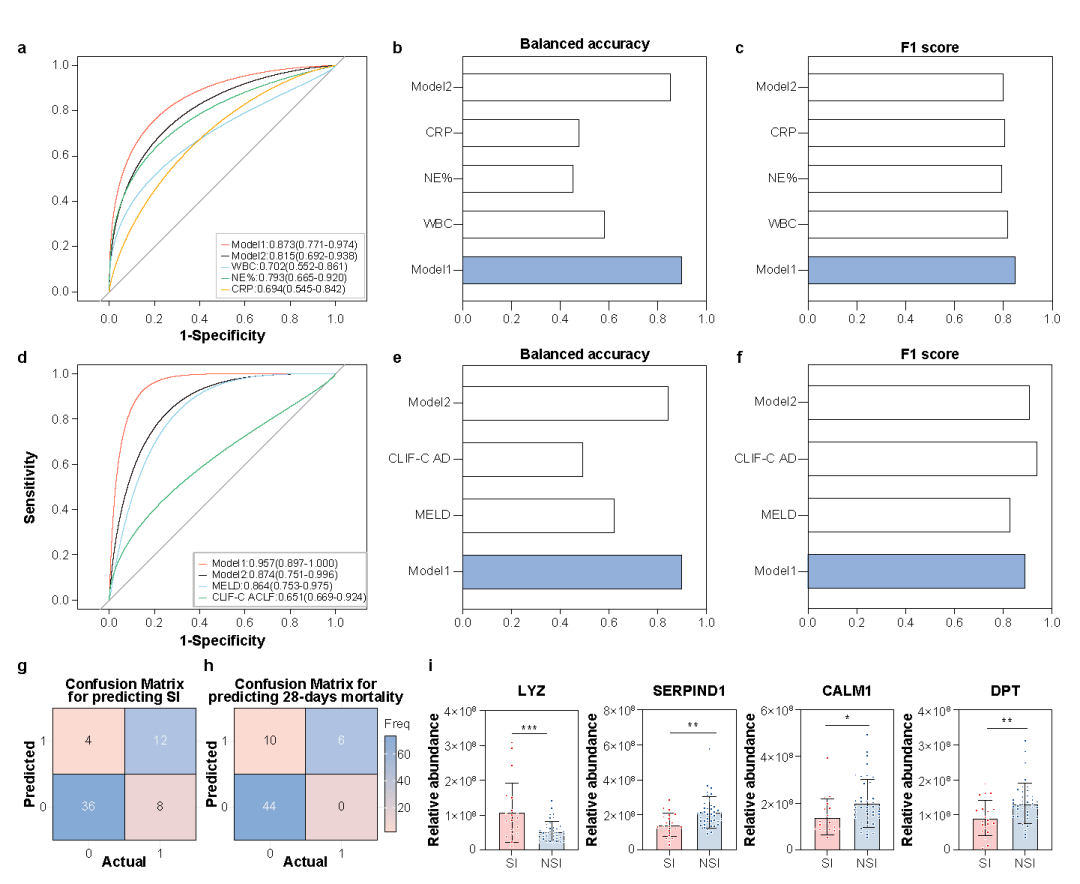 图5 模型在验证队列中的表现编辑
图5 模型在验证队列中的表现编辑
文章小结
本研究通过系统的蛋白质组学分析与机器学习建模,成功开发出可早期预测乙肝相关肝衰竭继发感染的风险评估模型。四个蛋白标志物(LYZ、CALM1、Serpin D1、DPT)与两个临床指标(AST、Tbil)的组合在多个独立队列中展现出优异的预测性能,并在ELISA平台上得到验证。该研究不仅揭示了炎症-凝血失衡在继发感染发病中的核心作用,更为临床提供了可在入院48小时内识别高危患者的实用工具,有望显著改善这类危重患者的临床预后。
拜谱小结
随着血液蛋白组学研究深入,大队列、高深度检测成为必然趋势。拜谱生物超高深度血液蛋白质组解决方案,以DB纳米磁珠富集技术打破传统局限,实现8000+蛋白稳定检出,覆盖大量低丰度功能蛋白,数据重复性与精准度行业领先。拜谱生物可提供“非靶向筛选-靶向验证-机器学习建模”一体化服务,助力科研人员突破鉴定深度不足、数据质量不佳的难题,高效挖掘疾病标志物、深化机制研究,加速科研成果向临床转化。若您正开展血液蛋白组相关研究,渴望提升检测深度与数据可靠性,欢迎联系我们,携手推动精准医疗迈上新台阶!
参考文献
Xiong F, Zheng J, Chen J,et,al. Proteomics-based machine learning model for predicting secondary infection in HBV-related liver failure. Nat Commun. 2026 Mar 3. doi: 10.1038/s41467-026-69075-y. Epub ahead of print. PMID: 41776162.